De la reconstruction virtuelle des faisceaux de matière blanche...
L'imagerie par résonance magnétique de diffusion (IRMd) permet de mettre en évidence in vivo les faisceaux de matière blanche du cerveau humain en mesurant la diffusion des molécules d'eau, notamment le long des axones. Il est alors possible par tractographie de reconstituer de proche en proche les trajets des faisceaux de fibres nerveuses représentés alors sous la forme d'un tractogramme (Figure 1).
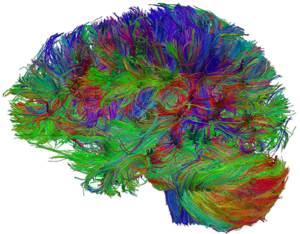
Figure 1 : Tractogramme représentant l'organisation anatomique de la matière blanche prise in vivo dans sa globalité. Il est fait de millions de fibres virtuelles dont le code couleur représente leur orientation dans la matière blanche et produit de remarquables représentations des principaux faisceaux.
… à la réalité de l'anatomie du cerveau humain.
Il existe un grand nombre d'algorithmes de tractographie, chacun avec sa propre capacité à reproduire au plus près l'organisation des fibres de matière blanche. Cependant, cette organisation est très complexe et il n'existe pas aujourd'hui de définitions exactes des trajectoires et terminaisons de toutes les fibres de matière blanche du cerveau humain. L'absence de cette réalité « terrain » rend difficile l'estimation du degré de fiabilité des différents algorithmes de tractographie.
Un défi a été lancé à la communauté scientifique de l'imagerie de diffusion et de la tractographie en 2015 (ISMRM 2015 Tractography challenge) : fournir la meilleure reconstruction tractographique possible d'un jeu de données d'imagerie de diffusion contenant un ensemble de faisceaux dont les trajectoires et les terminaisons étaient clairement identifiées. Les résultats de ce défi font l'objet de la présente étude.
Vingt groupes de recherche ont participé (Figure 2), soumettant 96 propositions distinctes de tractographie. Le plus encourageant a été de constater que la plupart des algorithmes de pointe actuels produisent des tractogrammes contenant 90% de faisceaux valides inclus dans les données de départ. Ces mêmes tractogrammes contiennent cependant beaucoup plus (trop !) de faisceaux invalides que valides, et la moitié des faisceaux invalides a été systématiquement identifiée par tous les groupes de recherche.
Cette vaste étude internationale démontre et confirme les ambiguïtés fondamentales inhérentes à la reconstruction des fibres blanches lorsqu'elle est uniquement basée sur l'information d'orientation de la diffusion des molécules d'eau. Ceci doit donc être pris en compte lors de l'interprétation des résultats de tractographie révélant la connectivité anatomique du cerveau humain.
En dépit de ses limites, la tractographie demeure aujourd'hui le seul outil permettant de cartographier la connectivité anatomique du cerveau humain in vivo. Nul doute que les résultats de ce défi vont favoriser le développement de nouveaux algorithmes de tractographie en intégrant notamment des connaissances anatomiques préalables afin d'améliorer les connaissances sur l'anatomie de la substance blanche et de construire des connectomes humains anatomiquement corrects.
Site du GIN-Bordeaux contact : Laurent Petit